摘要:北京化工大学吴边团队与中国科学院微生物研究所崔颖璐团队合作,借助人工智能驱动的微生物酶资源挖掘策略,成功发现了一种新型脲酶AbPURase。该酶具有优异的有机溶剂耐受性,在高浓度醇解反应介质中仍能保持极高催化活性与稳定性,与工业聚氨酯醇解工艺高度兼容。该成果首次实现了在工业条件下聚氨酯的规模化生物解聚,为聚氨酯塑料的绿色循环利用提供了高效、可持续的新路径。2025年10月30日,相关研究成果发表于《Science》。
聚氨酯塑料作为一种高分子聚合物,被广泛应用于汽车制造、绝缘材料、矿山机械及建筑工程等领域。理论上,可通过水解等化学方法将其解聚,回收原始单体实现循环利用,但这类材料具有高度交联的三维网络结构,导致其解聚过程条件苛刻,严重制约了其闭环再生的产业化进程。为实现聚氨酯的生物酶解,关键在于开发能够高效水解氨基甲酸酯键的脲酶。
基于此,研究人员开发了基于图神经网络的酶挖掘工具GRASE(GNN-based Recommen-dation of Active and Stable En-zymes)。该工具通过估算蛋白质序列与结构之间的似然性,预测蛋白质稳定性;并利用图神经网络提取催化口袋中氨基酸的局部微环境与整体结构信息,通过在高维空间中计算不同催化口袋特征向量之间的余弦相似度以度量其功能相似性,从而实现对酶底物特异性与反应偏好性的精细推断。
研究人员利用GRASE工具,从宏基因组数据中成功挖掘到多个具有氨基甲酸酯降解活性的酶,其中来源于脂环酸芽孢杆菌属的AbPURase酶表现出全方位的优异特性。该酶具有一个V形活性口袋,该结构由一个紧密的疏水核心及多个脯氨酸残基所稳定的盖结构域构成。这一独特的结构不仅有助于酶与底物的结合,还有效阻隔了有机溶剂分子向活性中心的渗透,从而保障AbPURase在高浓度有机溶剂中结构和功能的完整性。
得益于其独特的天然结构特性,AbPURase酶在工业醇解工艺中的高浓度二乙二醇环境中,活性高达已报道脲酶的465倍,显示出卓越的催化效率和极强的有机溶剂耐受性。在模拟工业化反应条件的千克级商业聚醚型聚氨酯泡沫降解实验中,AbPURase在8h内实现了98.6%的底物转化率,降解单体TDA及醇解剂DEG的回收率分别高达94.7%和98.5%。此外,AbPURase还表现出优异的操作稳定性,可在多轮循环中维持高降解活性,显示出该酶的工业应用潜力。
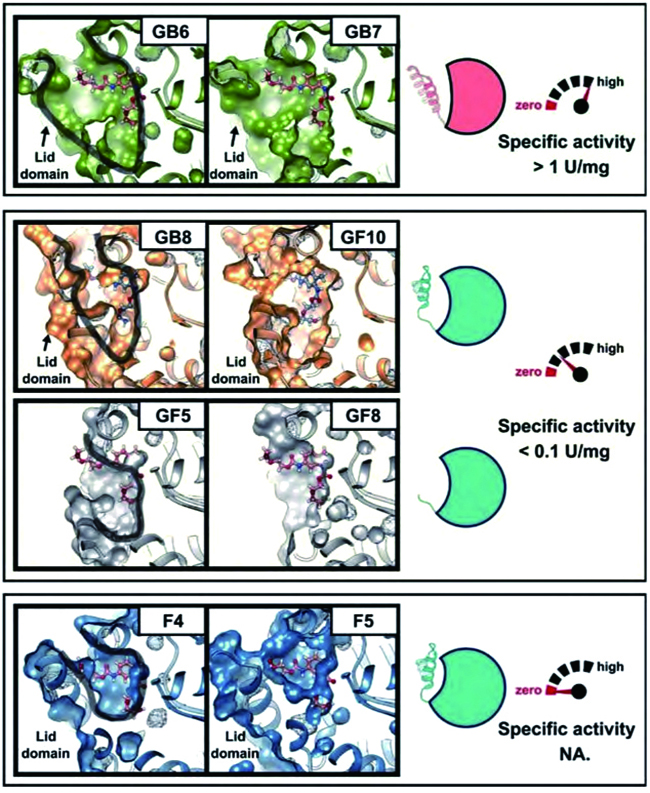
图片1不同酶活性位点口袋的局部结构差异凸显了盖结构在催化性能中的关键作用
(图片来源:《Science》)
该研究不仅为塑料循环利用提供了具备工业应用潜力的解决方案,还推动了人工智能在工业酶开发领域的智能化进程。













 玻纤含量对长玻纤...
玻纤含量对长玻纤... 钙钛矿薄膜的均匀...
钙钛矿薄膜的均匀... 用于光伏板静电除...
用于光伏板静电除... 聚砜医疗干粉吸入...
聚砜医疗干粉吸入...














